Archiv Detail
Verbesserter Gesundheitscheck für Fliessgewässer
2. Dezember 2019 |
Dreht man in einem Fluss oder Bach einen Stein um, so wimmelt es von kleinen Tieren: Köcherfliegen, Wasserkäfer, Bachflohkrebse und Schnecken. Die mit blossem Auge sichtbaren wirbellosen Organismen am Gewässergrund, Makrozoobenthos genannt, sind eher unscheinbar, doch für die Wissenschaft und den Gewässerschutz von grosser Bedeutung. Einzelne Arten dieser Gemeinschaft reagieren sehr empfindlich gegenüber Veränderungen in ihrer Umwelt, zum Beispiel auf Schadstoffe oder Verbauungen entlang des Ufers oder im Einzugsgebiet des Gewässers. Andere wiederum sind tolerant. Die Diversität der kleinen Tiere lässt daher wichtige Rückschlüsse auf die Wasser- und Gewässerqualität zu. Teils lässt sich sogar auf die Ursachen einer Verschlechterung des ökologischen Zustands zurückschliessen.
Schweizweite modellgestützte Analyse der wirbellosen Kleinorganismen
Erstmals haben nun die Eawag-Forschenden Nele Schuwirth und Bogdan Caradima gemeinsam mit weiteren Kollegen der Abteilung Systemanalyse und Modellierung kantonale und bundesweite Daten über das Makrozoobenthos gesamthaft untersucht. Sie nutzten hierfür die Datenbank für Makrozoobenthos MIDAT des Schweizerischen Zentrums für die Kartografie der Fauna (SZKF). Darin enthalten sind die Daten des Biodiversitätsmonitoring BDM, der Nationalen Beobachtung Oberflächengewässerqualität NAWA und von 14 kantonalen Monitoring-Programmen.
Da die Programme die wirbellosen Kleinlebewesen auf unterschiedlichen systematischen Niveaus – Familie, Gattung, Art – erfassen, mussten die Datensätze zuerst vereinheitlicht werden. Anschliessend haben die Forschenden sie mithilfe von statistischen Modellen analysiert und wichtige direkte und indirekte Einflussgrössen für das Auftreten einzelner Organismen identifiziert. Dies waren unter anderem Wassertemperatur, Insektizid-Anwendungen im Einzugsgebiet, Fliessgeschwindigkeit, Landwirtschaft und Bewaldung entlang des Ufers, Siedlungsfläche und Grossvieheinheiten im Einzugsgebiet. Einige dieser Einflussgrössen wie die Wassertemperatur beeinflussen die Organismen direkt. Andere dienen als Indikatoren für Einflussgrössen, die nicht direkt gemessen wurden. So kann zum Beispiel die Bewaldung des Uferbereichs zu erhöhtem Laubeintrag, Beschattung des Gewässers und vermindertem Eintrag von Nähr- und Schadstoffen aus dem Einzugsgebiet führen.
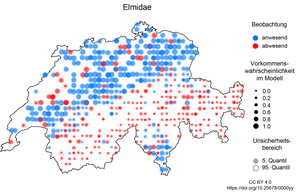
Vorkommen der Käferfamilie Elmidae in der Schweiz in den Biodiversitätsmonitoringdaten und im Modell, grosse blaue Punkte und kleine rote Punkte zeigen eine gute Übereinstimmung zwischen Beobachtung und Modell.
Aus den Ergebnissen haben die Forschenden Empfehlungen für das Design der Monitoring-Programme und das Gewässermanagement abgeleitet:
Identifikation von Ursachen durch Bestimmung der Arten
Seit 2010 werden Untersuchungen und Beurteilungen des Makrozoobenthos in Schweizer Fliessgewässern gemäss dem Bewertungsverfahren des Modul-Stufen-Konzepts durchgeführt. Vorgeschrieben ist dabei die Erfassung der Organismen auf dem Niveau der Familie. Die Modellanalyse bestätigt das Bewertungsverfahren weitgehend: Als sensitiv eingestufte Familien reagieren auch im Modell stärker auf Belastungen. Die Studie weist aber auch darauf hin, dass eine bessere taxonomische Auflösung, also die Bestimmung von Arten, wertvolle Zusatzaussagen ermöglichen würde. So liesse sich etwa besser identifizieren, welche spezifischen Ursachen die Wasser- oder Gewässerqualität beeinträchtigt haben könnten.
Mehr Daten, höhere Aussagekraft
Je mehr Daten für die Auswertung verfügbar sind, desto höher ist die Aussagekraft. Für zukünftige Analysen ist es daher essenziell, dass möglichst viele Monitoring-Programme ihre Daten sowie Zusatzformationen wie Substrat-Daten an die MIDAT-Datenbank liefern.
Einheitliche Monitoring-Konzepte
Heute werden in den Kantonen unterschiedliche Gruppen des Makrozoobenthos bis auf Artniveau bestimmt. Für eine schweizweite Auswertung wäre es jedoch sinnvoll, immer die gleichen Gruppen in dieser hohen taxonomischen Auflösung zu erfassen. Eine einheitliche Liste zur Artbestimmung wäre daher vorteilhaft. Die Studie der Eawag kann dazu beitragen zu beurteilen, für welche Gruppen sich das besonders lohnen würde.
Erweitertes Monitoring-Design
Um die Identifikation wichtiger Einflussfaktoren auf die Gewässerökologie zu verbessern, lohnt es sich, zusätzliche Stellen in die Monitoring-Programme aufzunehmen. Vor allem Stellen mit seltenen Kombinationen von Einflussfaktoren sind für die Analyse interessant, zum Beispiel Stellen mit niedriger Wassertemperatur und beeinträchtigter Wasserqualität.
Integrales Gewässermanagement
In Gewässern lebende Tiere und Pflanzen reagieren meist auf mehrere Stressfaktoren, zum Beispiel schlechte Wasserqualität, monoton hohe Fliessgeschwindigkeit und erhöhte Wassertemperaturen. Bei Massnahmen zur Verbesserung der Wasser- und Gewässerqualität ist es daher empfehlenswert, soweit möglich und nötig eine Kombination von Massnahmen umzusetzen, zum Beispiel eine Revitalisierung kombiniert mit der Aufrüstung der Kläranlagen und der Verminderung von Schadstoffeinträgen aus der Landwirtschaft flussaufwärts.
Eine ausführlichere Zusammenfassung der Ergebnisse haben Schuwirth und Caradima in der heutigen Ausgabe der Zeitschrift Aqua und Gas in Zusammenarbeit mit dem Bundesamt für Umwelt BAFU und dem Atelier für Naturschutz und Umweltfragen AG UNA publiziert: «Analyse schweizweiter Makrozoobenthosdaten: Erkenntnisse über anthropogene Einflüsse und Monitoring Design».
Originalpublikation
Schuwirth et al., «Analyse schweizweiter Makrozoobenthosdaten: Erkenntnisse über anthropogene Einflüsse und Monitoring Designhttps://www.eawag.ch/typo3/#_msocom_1», Aqua & Gas, Nr. 12/2019
Finanzierung
Die Modell-Studien wurden vom Bundesamt für Umwelt (BAFU) und dem EU Horizon 2020-Programme (Projekt Aquacross, Grant agreement No. 642317) mitfinanziert.