Détail de l'archive
Comment les facteurs de résistance se faufilent à travers les STEP
12 décembre 2018 |
Plus de 95 % des bactéries rejetées avec les excréments humains dans les eaux usées sont éliminées dans les stations d'épuration. Pourtant, de nombreuses bactéries résistantes aux antibiotiques sont détectables dans les effluents d'épuration. Comment est-ce possible ? Pour le savoir, le microbiologiste Helmut Bürgmann et son équipe ont observé le devenir des bactéries antibiorésistantes au cours des étapes de traitement de douze stations d'épuration (STEP). Ils ont par ailleurs cherché à savoir si les facteurs de stress présents dans les eaux usées – comme les antibiotiques, les biocides ou les métaux lourds – avaient une influence sur l'occurrence de l'antibiorésistance.
Un «noyau dur» d'irréductibles
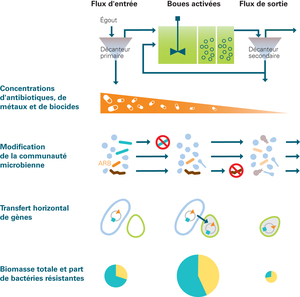
Dans chacune des douze STEP, les biologistes ont prélevé des échantillons de biomasse bactérienne en entrée et en sortie de station ainsi qu'au niveau du traitement secondaire. Ils en ont extrait et analysé l'ADN puis identifié les séquences géniques codant la résistance aux antibiotiques. Les résultats indiquent que l'antibiorésistance est plus faible dans les eaux traitées que dans les eaux usées brutes mais également, comme l'indique Helmut Bürgmann, que «le passage dans la station d'épuration s'accompagne d'une augmentation de la part relative de micro-organismes résistants».
Les scientifiques ont décelé une grande diversité de gènes de résistance dans l'ADN total de la communauté microbienne. Ils ont par ailleurs constaté que leur nature variait fortement au cours des traitements d'épuration mais qu'un petit groupe de gènes de résistance était présent à toutes les étapes. Ce «noyau dur» se faufile à travers la STEP où il est relativement fréquent. Ainsi, alors que près de 70 % des gènes de résistance arrivant à la STEP avec les eaux résiduaires sont éliminés par les traitements d'épuration, d'autres viennent en partie les remplacer. Bürgmann considère que «près de 40 % des gènes de résistance détectés en sortie de STEP proviennent probablement des boues activées».
Le graphique montre les processus possibles qui influencent la composition et la fréquence des gènes de résistance aux antibiotiques au cours de leur passage dans la STEP. La quantité totale de bactéries est maximale au niveau du traitement biologique et elle est beaucoup plus faible en sortie de STEP qu'en entrée. Toutefois, la part de bactéries résistantes augmente (zone jaune dans le camembert). On observe une accumulation d'antibiorésistance au sein de la communauté microbienne.
(Graphique : Liz Amman, Source : Bürgmann et al, 2018)
La résistance, gage de survie
Les microbiologistes supposent que les conditions de vie dans la STEP favorisent la survie des micro-organismes résistants. Le fait qu'il existe une corrélation entre la fréquence de l'antibiorésistance et la concentration de certains antibiotiques – au demeurant très faible dans la STEP – semble l'indiquer. Par ailleurs, les gènes de résistance restaient actifs dans toute la STEP, jusqu'à sa sortie. Pour Bürgmann, le fait que l'antibiorésistance soit fréquente dans les boues activées est lié à la promiscuité des micro-organismes dans la STEP : «Les gènes de résistance des bactéries intervenant dans le traitement biologique sont parfois identiques à ceux détectés chez les germes pathogènes. Il est probable qu'ils aient été acquis par échanges de gènes entre bactéries voisines.»
Des gènes mobiles
En plus des gènes de résistance en eux-mêmes, Helmut Bürgmann et son équipe ont donc également recherché – et trouvé – des gènes marqueurs d'éléments génétiques mobiles indicateurs d'échanges de matériel génétique entre bactéries différentes. Il s'est avéré que ces gènes marqueurs se trouvaient souvent à proximité immédiate de gènes de résistance et leur présence indique donc que des échanges conséquents de gènes de résistance s'effectuent entre les germes pathogènes venant des êtres humains et les autres bactéries. Comme le souligne Bürgmann, ce phénomène n'est pas sans conséquences : «Si des gènes de résistance sont transmis aux bactéries des boues activées et si ces dernières se disséminent dans l'environnement, elles y ont probablement de meilleures chances de survie que les germes pathogènes.» D'après le microbiologiste, le meilleur moyen de l'éviter est d'extraire totalement la biomasse de l'eau dans les STEP. Les nouvelles techniques progressivement mises en œuvre dans les stations d'épuration suisses pour éliminer les micropolluants y contribueront.