Détail de l'archive
Transposer la biologie en langage informatique
17 août 2021 |
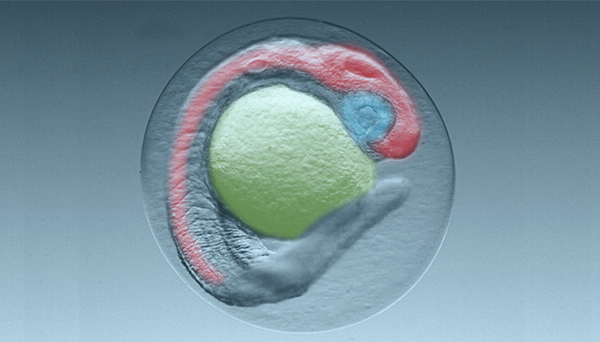
Chaque jour, une multitude de produits chimiques synthétiques se déversent par divers canaux dans les rivières, les lacs et parfois même jusque dans l’eau potable. L’institut de recherche de l’eau Eawag veut savoir quelles en sont les conséquences à long terme sur l’environnement aquatique et la santé humaine. «L’un des domaines de recherche les plus passionnants et complexes est la neurotoxicité, c’est-à-dire l’effet de ces substances sur le système nerveux – un domaine où nous avons encore peu de connaissances», explique Colette vom Berg, cheffe de groupe à l’Eawag. «Cela est dû au fait que le système nerveux est un réseau d’une très grande complexité où de nombreux facteurs interagissent», précise-t-elle. Ces connaissances seraient extrêmement utiles, car le cerveau en formation des embryons de vertébrés est en particulier très sensible aux influences extérieures. Certaines classes d’insecticides par exemple sont suspectées d’impacter le comportement des poissons en modifiant durablement le système nerveux en formation des embryons de poissons.
Le Big Data apporte de la lumière
À présent, les scientifiques qui travaillent avec Colette vom Berg, Anze Zupanic (ancien chef de groupe à l’Eawag) et le biologiste et postdoctorant Roman Li ont réussi à apporter un peu de lumière – et ce à l’aide du Big Data. «Pour cela, nous avons traduit la complexité biologique en langage informatique» explique Roman Li. Nous avons obtenu un modèle informatique qui représente les nombreux processus moléculaires du système nerveux en développement. Il nous permet de prédire de quelle façon différents produits chimiques peuvent endommager le système nerveux. La base du modèle est le poisson zèbre, un organisme modèle bien étudié en biomédecine et fréquemment utilisé en toxicologie.
Afin d’aborder le problème de la complexité, les scientifiques n’ont pas tenté de déceler l’effet toxique sur chaque gène ou protéine, mais ont utilisé pour leur modèle ce qu’on nomme le transcriptome. Ce terme réunit l’ensemble des gènes activés dans tout l’organisme à un moment donné. Il s’agit donc d’une sorte d’indicateur de l’état de l’organisme. Plus clairement: chaque substance agissant sur l’organisme active d’autres gènes.
Les chercheuses et chercheurs ont ensuite relié ce modèle d’activité aux possibles effets neurotoxiques sur l’organisme. Ils peuvent donc lire sur leur modèle informatique si une substance peut provoquer par exemple des convulsions, des troubles du rythme du sommeil, une microcéphalie (cerveau trop petit) ou une hydrocéphalie (accumulation de liquide dans le cerveau), et comment. On sait par exemple que l’acide domoïque (une substance produite par les cyanobactéries) provoque des convulsions sur les poissons, qui se mettent alors à tourner en rond. «Le modèle indique un mécanisme moléculaire qui pourrait être à l’origine de ce comportement», explique Roman Li.
Visualisation du modèle complet avec 344 nœuds. Les nœuds colorés représentent les trajets des signaux sélectionnés (graphique: Eawag, Roman Li)
Utilité pour l’homme et l’environnement
«Nous comprenons mieux à présent ce qui pourrait se passer au niveau moléculaire dans le système nerveux de l’embryon du poisson zèbre s’il est exposé de manière aiguë ou chronique à des produits chimiques», déclare Colette vom Berg. De cette façon, les chercheuses et chercheurs espèrent notamment réussir aussi à identifier les gènes ou les trajets des signaux qui serviraient de marqueurs pour la neurotoxicité: «Au lieu d’étudier tout le transcriptome, on pourrait rechercher seulement de manière ciblée l’activité de ce gène pour obtenir une indication du niveau de toxicité d’une substance déterminée sur le système nerveux» ajoute la cheffe de groupe.
Disponible librement en ligne
De plus, les chercheuses et chercheurs considèrent que leur modèle, disponible librement en ligne pour les scientifiques qui s’y intéressent selon la stratégie de science ouverte de l’Eawag, peut avoir un large domaine d’application. Roman Li explique: «Il peut s’utiliser pour la recherche fondamentale, mais aussi pour le développement de médicaments et, naturellement, en toxicologie. Il est donc au service de la santé humaine, mais aussi de la santé de notre environnement naturel.»
Photo de couverture: Eawag, Colette vom Berg
Publication originale
Financement / Coopérations
- Eawag
- National Institute of Biology, Slowenien
- Philip Morris International